自作関数の高速化
efficient R programingを読んでいて今後使えそうなことに関するメモ。
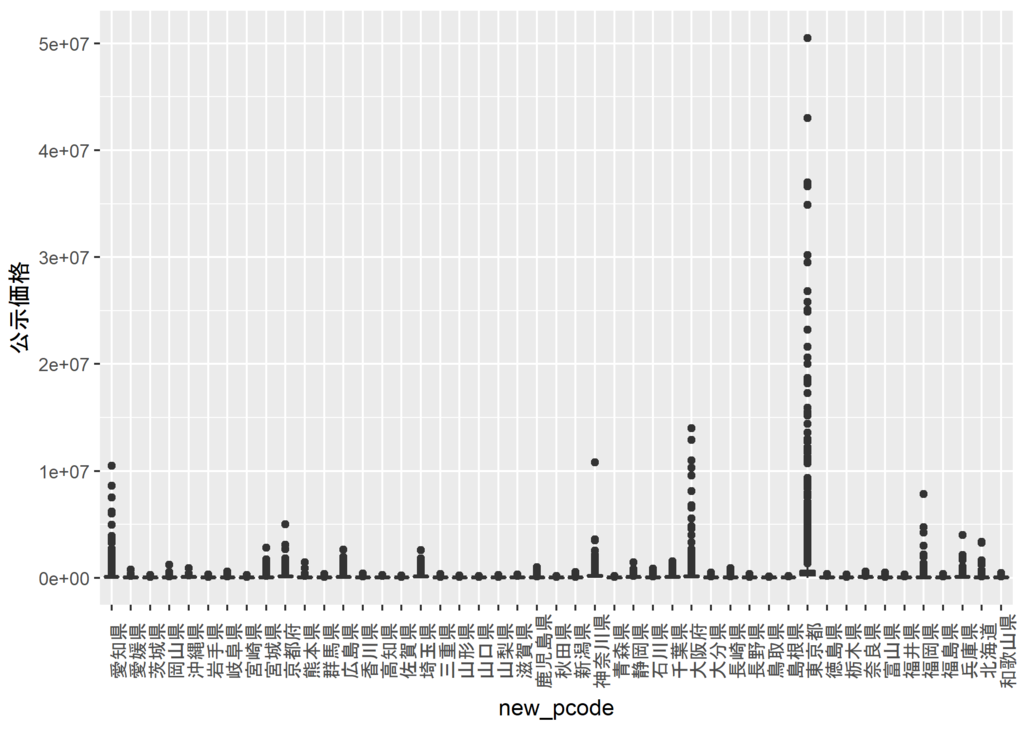
3.7 では自作関数の高速化について述べられている。
自作関数にcompiler::cmpfun()を適用すればよいだけらしい。
library(compiler) mean_r = function(x) { m = 0 n = length(x) for(i in seq_len(n)) m = m + x[i] / n m } cmp_mean_r = cmpfun(mean_r)
平均を求める関数についての比較結果はこのようになる。 結構差が出ているので、複雑な処理をする際には有効に使えそうである。
x = rnorm(1000) microbenchmark(times = 10, unit = "ms", # milliseconds mean_r(x), cmp_mean_r(x), mean(x)) #> Unit: milliseconds #> expr min lq mean median uq max neval cld #> mean_r(x) 0.358 0.361 0.370 0.363 0.367 0.43 10 c #> cmp_mean_r(x) 0.050 0.051 0.052 0.051 0.051 0.07 10 b #> mean(x) 0.005 0.005 0.008 0.007 0.008 0.03 10 a
tmapとggplot2の出力結果の比較
空間データのプロット
sfやspクラスオブジェクトのデータをプロットする方法について
tmapとggplot2パッケージによる出力を比較してみる。
library(tmap) library(sf) library(mapview) library(ggplot2)
spクラスオブジェクトとsfクラスオブジェクトの2つを準備する。
nc <- st_read(system.file("shape/nc.shp", package="sf"), quiet = T) data("atlStorms2005") class(nc)
[1] "sf" "data.frame"
class(atlStorms2005)
[1] "SpatialLinesDataFrame" attr(,"package") [1] "sp"
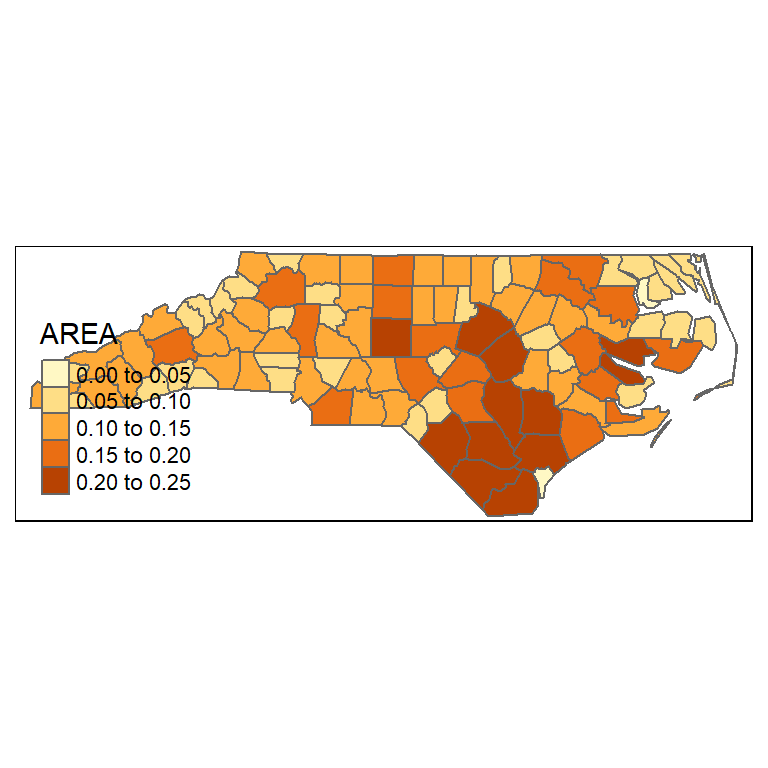
tmapを利用して書くと
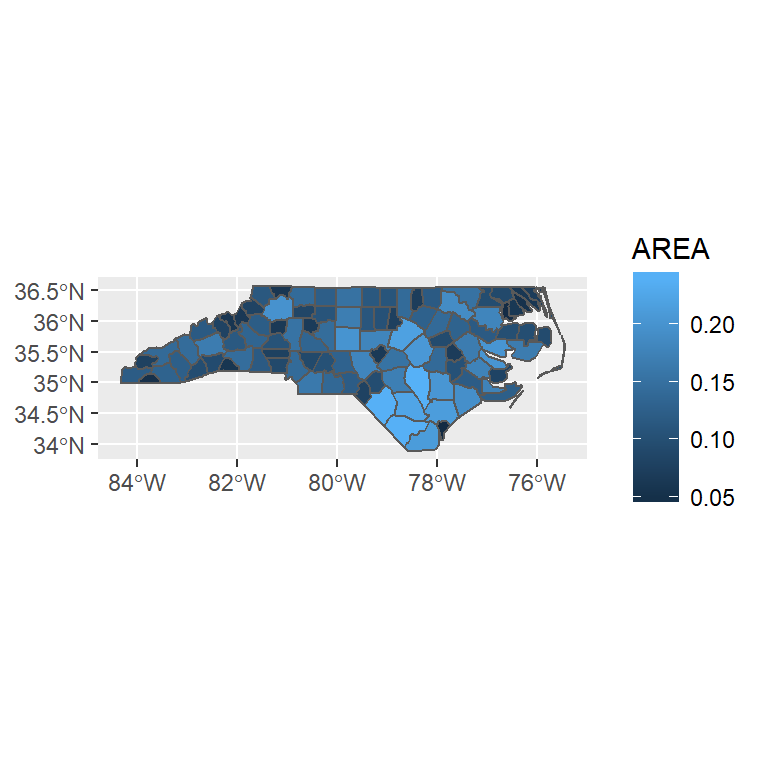
tm_shape(nc) + tm_polygons(col = "AREA")
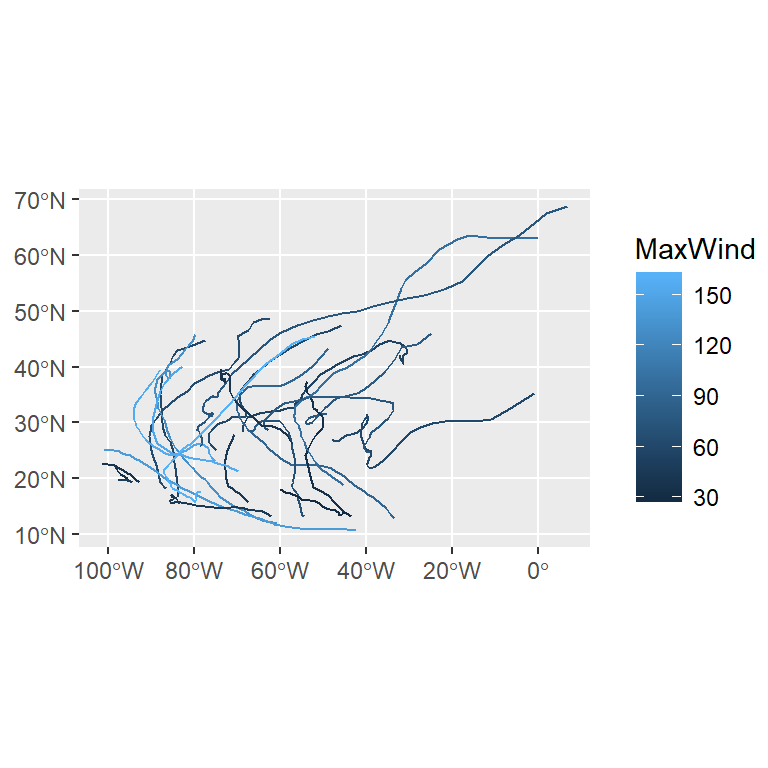
tm_shape(atlStorms2005) + tm_lines(col = "MaxWind") + tm_layout(frame = F)

ggplot2を利用して書くと
ggplot() + geom_sf(data = nc, aes(fill = AREA))
ggplot() + geom_sf(data = st_as_sf(atlStorms2005), aes(color = MaxWind))
tmapパッケージではsp, sfオブジェクトともに区別なく書くことができるが、
ggplot2ではsfオブジェクトのみ対応しており、変換が必要になる。
ggplot2パッケージのパレットが見づらいと感じるので、 デフォルトのパレットを変更されることを期待している。
行の結合にはrbind.fill()が便利
各データフレームを行で結合したい場合がある。
列で結合する場合はleft_join()などのjoin関数がある。
データがない部分はNAで保管される。
library(plyr) rbind.fill(mtcars[c("mpg", "wt")], mtcars[c("wt", "cyl")])
mpg wt cyl
1 21.0 2.620 NA
2 21.0 2.875 NA
3 22.8 2.320 NA
4 21.4 3.215 NA
5 18.7 3.440 NA
6 18.1 3.460 NA
.................
59 NA 2.140 4
60 NA 1.513 4
61 NA 3.170 8
62 NA 2.770 6
63 NA 3.570 8
64 NA 2.780 4
- 2017/7/23追記
dplyrパッケージのbind_rows()、rbind_all()関数でも同様のことができるらしいので、 わざわざplyrパッケージをロードして使用する必要もないらしい。 ただし、bind_rows()はオブジェクトクラスによってはうまく機能しないらしいので注意。 現時点ではsfオブジェクトに対してはエラーが発生する。
leaflet、mapviewパッケージを用いた可視化のコードサンプル
いつも調べながら書いているので、 よく利用するオプションを書いておく
# 必要とするパッケージ library(mapview) library(kokudosuuchi) library(tidyverse) library(sp)
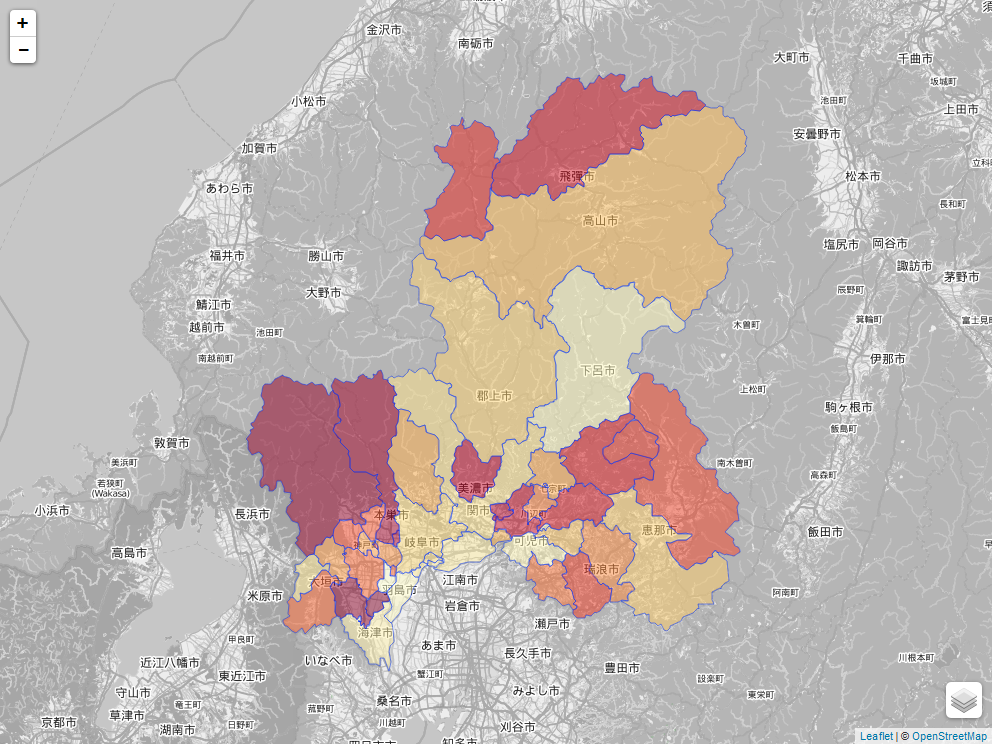
# データの読込(岐阜県の行政区域) getURL <- kokudosuuchi::getKSJURL("N03", prefCode=21) %>% filter(year == 2017) %>% .[,"zipFileUrl"] adm_area <- kokudosuuchi::getKSJData(as.character(getURL)) adm_area <- adm_area[[1]] proj4string(adm_area) <- CRS("+init=epsg:4612")
# mapview,leafletパッケージを用いて可視化 pal <- colorFactor(palette = "YlOrRd", domain = adm_area$市区町村名) leaflet() %>% addProviderTiles("OpenStreetMap.BlackAndWhite") %>% addPolygons(data = adm_area, weight = 1, group = "adm area", fillColor = ~ pal(adm_area$市区町村名), fillOpacity = 0.5, highlightOptions = highlightOptions(color = "green", weight = 7), popup = popupTable(adm_area@data)) %>% addLayersControl(overlayGroups = c("adm area"), position = "bottomright") %>% # mapview::mapshot(url = "test.html") # 静的な図として保存する場合はコメントアウト
data.frameからsfクラスのデータを作成する方法
結論から言うとst_as_sf(data.frame, coords=c(x, y), crs=4612)というように行えばよい
library(sp) library(sf) data(meuse)
head(meuse) ## x y cadmium copper lead zinc elev dist om ffreq soil lime landuse ## 1 181072 333611 11.7 85 299 1022 7.909 0.00135803 13.6 1 1 1 Ah ## 2 181025 333558 8.6 81 277 1141 6.983 0.01222430 14.0 1 1 1 Ah ## 3 181165 333537 6.5 68 199 640 7.800 0.10302900 13.0 1 1 1 Ah ## 4 181298 333484 2.6 81 116 257 7.655 0.19009400 8.0 1 2 0 Ga ## 5 181307 333330 2.8 48 117 269 7.480 0.27709000 8.7 1 2 0 Ah ## 6 181390 333260 3.0 61 137 281 7.791 0.36406700 7.8 1 2 0 Ga ## dist.m ## 1 50 ## 2 30 ## 3 150 ## 4 270 ## 5 380 ## 6 470
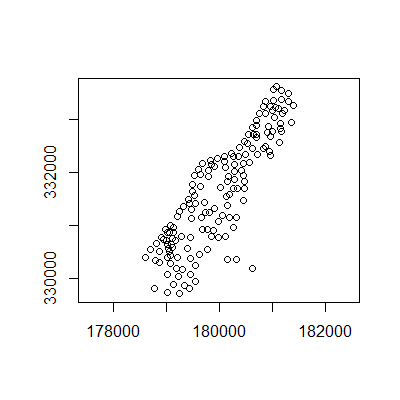
meuse_sf <- st_as_sf(meuse, coords = c("x", "y"), crs = 28992)
class(meuse_sf) ## [1] "sf" "data.frame"
meuse_sf %>% st_geometry() %>% plot(axes=T)
sfクラスのデータ抽出
ポリゴン内のポイントまたはポイントがあるポリゴンデータを抽出したい場合がある.
特に難しいことはないが,メモとして残しておく.
library(sf) set.seed(1) nc <- system.file("shape/nc.shp", package="sf") %>% st_read nc1 <- nc[1:50, ] nc_points <- st_sample(nc, size = 10) # plot(nc) plot(st_geometry(nc), border = "grey40") # plot(nc1) plot(st_geometry(nc1),border="grey40", col = "grey90", add = T) # plot(nc_points) plot(nc_points, add =T, pch = 16) # plot(nc1_filtered) nc1[nc_points, ] %>% plot(add=T, lwd = 2, border = "blue") # plot(nc_points_filtered) nc_points[nc1] %>% plot(add = T, col = "violet", cex = 3, lwd = 2)